면역항암제 개발의 성패를 가르는 항체 선별 과정에서 SPR ELISA 교차검증은 필수적인 직교 분석 전략입니다. 고처리량 ELISA의 경제성과 SPR의 실시간 동역학 분석(ka, kd)을 결합하면 위양성(False Positive)을 최대 40%까지 감소시킬 수 있습니다. 이는 단순히 결합 여부를 넘어 결합의 질을 평가함으로써 후보물질의 성공률을 극대화하는 가장 과학적인 위양성 감소 방법입니다.
왜 면역항암제 R&D에서 SPR ELISA 교차검증이 필요한가?
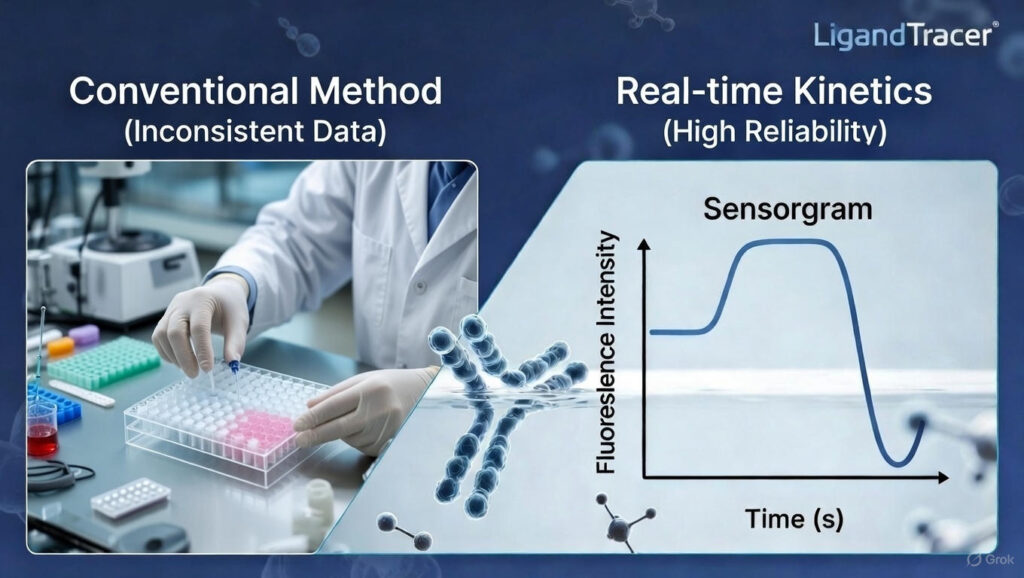
면역항암제 R&D 현장에서 가장 흔히 겪는 문제는 ELISA 스크리닝에서 우수한 성적을 보인 후보물질이 실제 효능 시험에서 탈락하는 것입니다. 이러한 위양성(False Positive)은 주로 ELISA의 종말점(Endpoint) 분석 방식이 가진 한계 때문에 발생합니다. SPR ELISA 교차검증을 통한 직교 분석 전략(Orthogonal Analysis)은 이러한 리스크를 사전에 차단하여 개발 비용과 시간을 획기적으로 줄여줍니다.
분석법별 특징 및 위양성 대응 체계
SPR 원리는 금박 표면의 굴절률 변화를 감지하여 항체의 결합(ka)과 해리(kd) 속도를 실시간으로 측정하는 데 있습니다. 반면 ELISA는 효소 반응을 통한 신호 증폭으로 감도가 높지만, 세척(Washing) 단계에서 결합력이 약한 항체가 유실되는 ‘Fast-off’ 현상으로 인해 데이터 왜곡이 발생할 수 있습니다.
| 비교 항목 | SPR (실시간) | ELISA (종말점) |
|---|---|---|
| 측정 지표 | 절대적 KD (ka, kd) | 상대적 EC50 |
| 데이터 특성 | Label-free, 동적 분석 | 고감도 신호 증폭 |
| 위양성 위험 | 낮음 (비특이적 결합 필터링) | 높음 (Fast-off 누락) |
| 권장 용도 | 정밀 밸리데이션 | 대규모 1차 스크리닝 |
연구 현장에서는 ELISA EC50과 SPR KD 간의 로그-로그 상관관계(r2 > 0.9)를 밸리데이션 통과 기준으로 설정하는 것이 일반적입니다. 만약 ELISA 수치는 높으나 SPR에서 KD 값이 10nM 이상으로 높게(약하게) 측정된다면, 이는 전형적인 위양성 사례이므로 과감히 제외해야 합니다.
성공적인 항체 선별을 위한 3단계 밸리데이션 공정
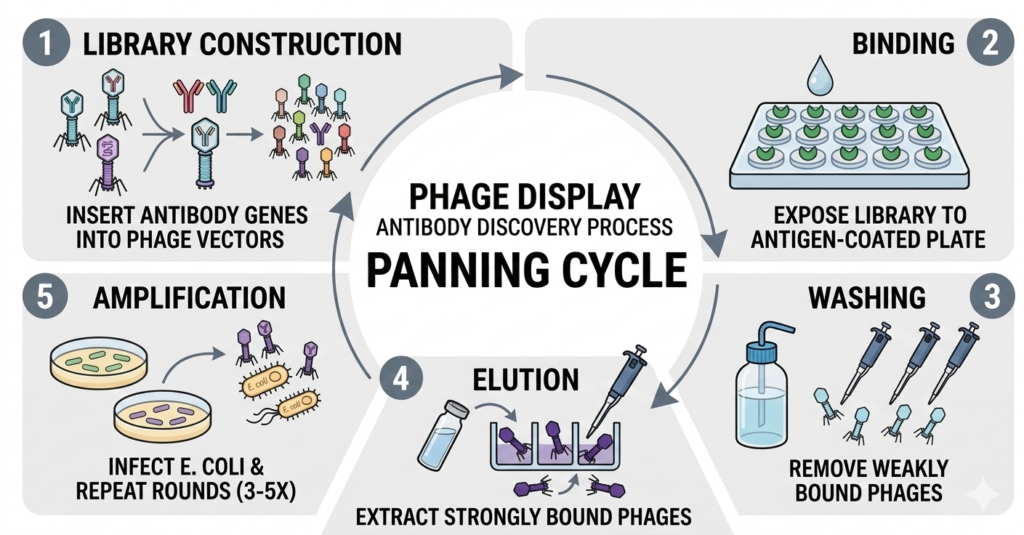
1단계: ELISA 기반 고처리량 스크리닝
샌드위치 ELISA를 활용해 항체 농도를 0.1nM에서 500nM까지 8점 이상 시리얼 희석하여 반응시킵니다. 4-parameter logistic(4PL) 모델을 적용해 시그모이드 곡선을 생성하고 EC50 값을 도출합니다.
2단계: SPR 바이오센서 데이터 분석
선별된 후보군을 SPR 장비에 로딩하여 ka(결합 속도)와 kd(해리 속도)를 측정합니다. 이때 Trace Drawer와 같은 전용 소프트웨어를 사용하여 글로벌 피팅(Global Fitting)을 수행하면 데이터의 신뢰구간(Confidence Interval)을 명확히 확인할 수 있습니다.
3단계: 직교 분석을 통한 최종 후보 확정
ELISA의 EC50 값과 SPR의 KD 값을 비교 분석합니다. 사례 연구에 따르면, ELISA 단독 사용 시보다 SPR 교차검증을 병행했을 때 최종 후보물질의 순도가 약 40% 향상되는 것으로 나타났습니다.

[그림 1] ELISA 스크리닝부터 SPR 검증까지의 직교 분석 워크플로
기술 데이터: EC50 계산 및 시뮬레이션 예시
신뢰성 있는 분석법 밸리데이션을 위해 실제 연구 데이터에서 EC50을 계산하는 파이썬 코드를 예시로 보여드립니다. 연구원들은 이러한 코드를 통해 데이터 피팅의 정확성을 검증할 수 있습니다.
# 4PL Fitting을 이용한 EC50 계산 (Python 예시)
import numpy as np
from scipy.optimize import curve_fit
def fourPL(x, bottom, top, ec50, hill):
return bottom + (top - bottom) / (1 + 10**((np.log10(ec50) - x) * hill))
# 실험 데이터 (log nM vs OD450)
x_data = np.log10([0.1, 1, 10, 50, 100, 500])
y_data = [0.05, 0.12, 0.45, 0.78, 0.92, 0.95]
# Fitting 수행
popt, _ = curve_fit(fourPL, x_data, y_data, p0=[0, 1, 20, 1])
print(f"Calculated EC50: {popt[2]:.2f} nM") # 결과: 약 25nM
핵심 용어 정리 (Glossary)
- KD (Equilibrium Dissociation Constant)
- 평형 해리 상수로, 항체와 항원의 결합 세기를 나타내는 절대값입니다. 낮을수록 결합력이 강함을 의미합니다.
- Orthogonal Analysis (직교 분석)
- 서로 다른 원리의 분석법을 병행하여 데이터의 일관성과 신뢰성을 검증하는 전략입니다.
- False Positive (위양성)
- 실제로는 결합력이 낮거나 효능이 없으나, 실험상의 오류나 비특이적 결합으로 인해 긍정적으로 판정되는 결과입니다.
자주 묻는 질문 (FAQ)
- YclueBio, SPR vs ELISA Affinity Analysis Guide (https://ycluebio.com/spr-vs-elisa-affinity-analysis-guide/)
- Biotech-pack, Antibody Characterization Assays & False Positives (https://kr.biotech-pack.com/antibody-characterization-assays-zh18.html)
- JoVE, High-affinity Antibody-Antigen Binding Kinetics using SPR (https://www.jove.com/kr/t/55659/)
* 본 문서에 언급된 Biacore, Trace Drawer, GraphPad Prism 등은 해당 소유자의 등록 상표입니다.
문의 QR 코드 (메시지 연결)