SPR 데이터만으로 부족한 항체 효능 검증, LigandTracer로 ‘진짜 결합력’을 확인해야 하는 이유
“수치적으로 완벽했던 항체가 왜 뇌 장벽(BBB) 앞에서는 침묵할까요?”
높은 결합력과 효능을 보였던 후보 물질이 In-vivo(동물 실험) 단계에서 실패하는 원인은 단순합니다. 인공적인 정제 환경에서 측정된 데이터가 실제 세포의 복잡한 결합력(Affinity)의 불균형을 잡아내지 못했기 때문입니다.
중추신경계(CNS) 질환 치료제를 연구하는 과정에서 가장 절망적인 순간은 세포 실험(In-vitro)의 압도적 성과가 실제 뇌 조직 전달 단계에서 무력해질 때입니다. 데이터의 공백을 메꾸지 못한 채 반복하는 ‘시행착오’는 연구의 효율을 떨어뜨릴 뿐만 아니라 귀중한 리소스를 낭비하게 만듭니다.
1. 현재 신약 개발 SPR 분석의 한계: 왜 동물 실험 결과가 다를까?
항체 및 신약 후보 물질 스크리닝의 표준인 신약 개발 SPR 분석은 정제된 단백질을 칩에 고정하여 상호작용을 측정합니다. 하지만 실제 혈액뇌관문(BBB)의 내피세포는 살아있는 유기체입니다.
RMT(Receptor-mediated transcytosis)의 정밀 제어
성공적인 BBB 셔틀을 위해서는 수용체와 결합한 후 세포를 가로질러 방출되는 과정이 정교하게 이루어져야 합니다. 이때 항체 효능 검증의 핵심은 결합 속도(ka)와 해리 속도(kd)의 미묘한 균형입니다. 결합이 너무 강하면 세포 내에 갇히고(Trap), 너무 약하면 전달되지 못합니다.
2. 성공적인 BBB 셔틀을 위한 필수 전략, LigandTracer의 역할
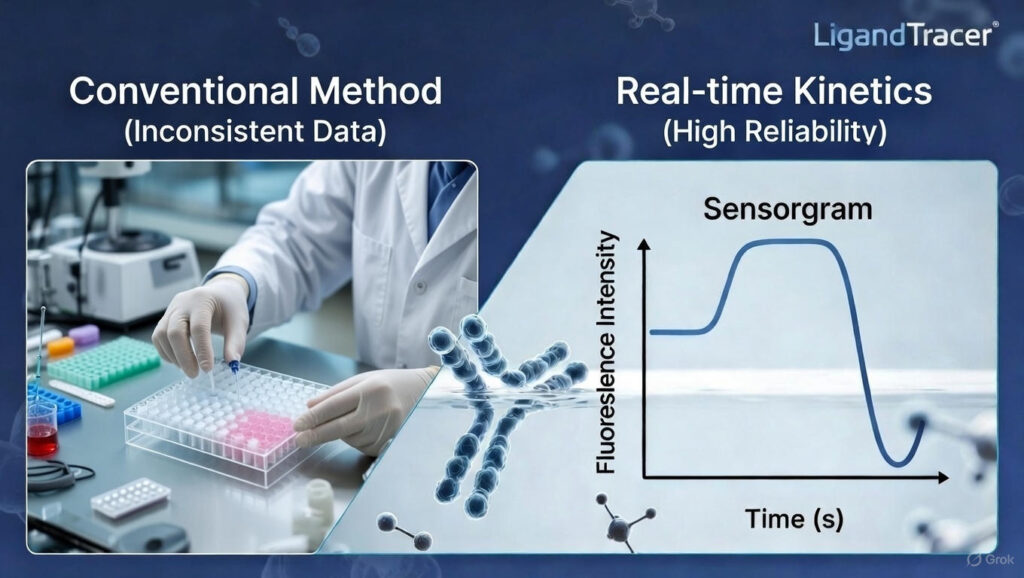
기존 분석 체계의 사각지대를 해결하기 위해 제시된 솔루션이 바로 LigandTracer(리간드트레이서)입니다. 살아있는 세포를 배양한 상태 그대로 분석하기 때문에 정제 단백질 분석에서는 알 수 없었던 ‘진짜 결합 패턴’을 포착합니다.
| 분석 항목 | 신약 개발 SPR 분석 (정제형) | LigandTracer (세포 기반) |
|---|---|---|
| 분석 대상 | 정제 단백질 (Purified) | 살아있는 세포 (Living Cell) |
| 환경 모사 | 인공적 환경 | 생리적 환경 (Physiological) |
| 내입(Internalization) | 확인 불가 | 실시간 관찰 및 측정 가능 |
| 주요 장점 | 초정밀 분자 결합력 확인 | 세포 내 유효성 및 기전 증명 |
3. 데이터로 증명하는 항체 효능 검증: 성공 사례
상위 저널에 게재되는 논문들은 SPR과 LigandTracer 데이터를 상호 보완적으로 제시하여, 분자 수준과 세포 수준 모두에서 결합력이 최적화되었음을 증명하고 있습니다. 이는 심사위원들에게 데이터의 완결성을 어필하는 가장 강력한 무기가 됩니다.
4. 연구 효율을 높이는 결단: 데이터 신뢰도가 곧 경쟁력입니다
원인을 모른 채 반복하는 ‘노가다’식 실험은 이제 멈춰야 합니다. 정밀 분석 장비로 도출된 Sensorgram 한 장은 수만 마디의 부연 설명보다 강력한 확신을 줍니다. 와이클루바이오는 여러분의 샘플이 가진 잠재력을 수치로 증명할 수 있도록 최적의 분석 환경을 지원합니다.
성공적인 BBB 셔틀 연구를 위한 기술 지원
여러분의 소중한 샘플, 결합력 데이터에 답이 있습니다.
와이클루바이오가 제공하는 특별한 분석 솔루션을 만나보세요.
- ✅ LigandTracer 활용 실시간 세포 결합 테스트 지원
- ✅ 전문가의 SPR 데이터 해석 및 컨설팅 가이드 제공
- ✅ 논문 게재율을 높이는 고해상도 데이터 생성
LigandTracer 분석 및 렌탈 문의하기
Björke, H., & Andersson, K. (2018). Measuring the affinity of drug-target interactions in a physiological environment using LigandTracer. Journal of Molecular Recognition, 31(11), e2733.
Nygren, P. Å., & Andersson, K. (2020). Real-time analysis of biomolecular interactions on living cells. Expert Review of Proteomics, 17(2), 101-112.